首页
Biopython分析重复结构
Biopython分析重复结构
时间: 2023-10-01 13:07:29
浏览: 45
可以回答如下: Biopython是一个专门用于生物信息学相关任务的Python库。其提供了很多方便的工具和方法,可以快速完成一些生物信息学任务,包括序列处理、结构分析等。在分析重复结构方面,可以使用Biopython中的一些方法,比如SeqRecord和SeqIO来读取和处理序列数据,使用Seq类来进行序列比对,使用PairwiseAlignment类来分析序列之间的相似性等。
阅读全文
相关推荐
基于Python的重复元素判断.docx
重复元素判定 一、用set方法去重后与原列表长度比较 lst=[1,3,5,3,4,4,2,9,6,7] set_lst=set(lst) #set会生成一个元素无序且不重复的可迭代对象,也就是我们常说的去重 if len(set_lst)==len(lst): print('列表里的元素互不重复!') else: print('列表里有重复的元素!') 二、用append的方式把原列表中的元素添加到一个新列表,确保新列表里不存在重复的元素,然后比较两个列表 lst=[1,3,5,8,9,9,0,0,3,3] new_list=[] for i in lst: if i not in new_list: new_list.append(i) #这样能确保新的列表里包含原列表里所有种类的元素,且元素互不重复 if len(new_list)==len(lst): print('原列表里的元素互不重复!') else: print('原列表里有重复的元素!')
python解析含有重复key的json方法
python自带的json包能够方便的解析json文本,但是如果json文本中包含重复key的时候,解析的结果就是错误的。如下为例 {"key":"1", "key":"2", "key":"3", "key2":"4"} 经过解析,结果却如下所示: { "key":"3", "key2":"4" } 原因是python解析的时候是创建一个字典,首先会读取到key的值,但是后面遇到重复键的时候,后来的值会覆盖原来的值,导致最后只有一个key的值留下来。 这肯定不是我们想要的结果,其中一种结果可以是将相同键的值聚合成一个数组,即如下所示。 { "key":["1","2","
biopython中文指南
在BioPython中可以发现多个模块,它们涵盖了序列处理、蛋白质结构分析、分子进化模拟、基因组学分析、图形绘制等多个方面。BioPython的安装过程通常涉及Python环境的搭建和BioPython包的安装。对于非Python开发者来...
biopython-冠状病毒:Biopython Jupyter Notebook教程,描述小基因组
Biopython是生物学数据处理和分析的开源工具,它为处理序列、结构、比对、进化和数据库查询等任务提供了丰富的功能。Jupyter Notebook作为一个交互式计算环境,使得我们能够方便地结合代码、文本、图像和输出结果,...
面向生信专业的数据结构与算法,选用Python语言,以理解原理、掌握应用为主
在生物信息学领域,理解和掌握数据结构与算法是至关重要的,因为它们构成了处理大量基因组数据和生物序列分析的基础。本教程重点在于使用Python语言来教授这些核心概念,旨在帮助生信专业人员深入理解原理,并能熟练...
缅甸蟒养殖种群的遗传多样性分析.pdf
对于专业指导和数据分析,Python作为一个强大的编程语言,能够通过相关的数据科学和生物信息学库(如NumPy、SciPy、Biopython等)对遗传数据进行高效的分析处理。 综上所述,文章通过对缅甸蟒养殖种群的遗传多样性...
Biopython教程:解读位置权重矩阵在生物信息学中的应用
模体通常是指在多个序列中重复出现的短片段,它们可能代表了某种功能或结构特征。.counts属性提供了这些核苷酸出现的原始计数值。为了得到位置权重矩阵,我们需要对这个计数矩阵进行标准化,即除以序列中的实例...
DupRemover工具:高效去除FASTA文件中的重复序列
这对于DNA、RNA或蛋白质序列分析是非常有用的,因为重复序列可能会干扰分析的准确性和结果的解释。通过移除重复项,DupRemover有助于确保数据集的准确性和一致性。DupRemover使用了Biopython库,这是一个免费且开源...
Python实现的PHYS 380蛋白质分析中期代码
Python有众多库,如Biopython、NumPy、SciPy、Pandas和Matplotlib,这些库提供了强大的数据处理和分析工具,能够支持基因组学、蛋白质组学、生物统计学和生物网络分析等生物信息学研究。 3. 计算机模拟在蛋白质研究...
蛋白质互作建模:ppi_feature_trees分析
资源描述中提到需要安装Prody库,这是一个专门用于蛋白质结构分析和动力学模拟的Python工具包。Prody能够处理PDB文件(蛋白质数据银行文件),并提供了强大的功能来分析蛋白质的结构和动态特性。使用Prody,研究人员...
KU Leuven课程项目:组学技术和数据分析
文件中提到的“项目文件夹结构”没有具体说明,但是通常包含脚本、数据文件、配置文件等,这些文件用于构建CRISPR区域分析的流程。文件夹结构的设计取决于项目的需求,比如是否采用模块化的方式组织代码,是否将测试...
GENMOD:注释遗传模式并分析基因组变异的工具
它支持多种模块和库,比如Pandas用于数据分析,Biopython用于生物计算等,使得处理生物数据和执行相关分析变得更加高效。GENMOD的开发采用Python语言,说明了Python在基因组学数据分析中的实用性。 6. vcf文件解析 ...
基因组学中的重复序列分析技术
在细胞功能方面,重复序列可以影响染色体的稳定性和染色体结构的形成。例如,端粒重复序列在染色体末端形成端粒,可以保护染色体不受损伤,维持染色体的稳定性。此外,重复序列还参与了基因的调控、转录和翻译等过程...
【提升进化树分析】:5个实用技巧,快速提高系统发育分析效率
重点探讨了进化树分析中的关键算法,如最大似然法、最小进化法和邻接法,以及进化树的构建原理,包括树的拓扑结构、分支长度解释和稳定性评估。同时,本文也对进化树分析的统计学基础和常用软件工具进行了详细讨论,...
转录组测序技术及数据分析
转录组测序技术的原理主要涉及mRNA的逆转录合成cDNA、文库构建、测序以及数据分析等步骤。转录组测序可以帮助研究人员全面了解特定生物样品的基因表达情况,从而揭示基因调控网络、发现新基因、识别变异等,对于深入...
序列与序列分析:认识与探索
本文将从序列的基本概念、分析方法、应用案例以及技术挑战与发展趋势等方面进行深入探讨,希望能够全面地介绍和解析序列分析这一重要领域。 ## b. 目的 本文的目的是介绍序列分析的基本概念、常用方法和工具,以及...
Python在遗传数据分析中的高级技巧
遗传数据分析作为生物信息学研究中的一项重要技术,近年来得到了飞速的发展。Python作为一门功能强大的编程语言,在遗传数据分析领域同样扮演着关键的角色。本章将介绍遗传数据分析所需的Python基础知识,为读者打造...
Python在药物研发中的数据分析应用
从化合物筛选到临床试验数据分析,Python提供了一系列工具和框架,极大地加速了药物研发的进程。 ## Python的跨学科优势 Python不仅在IT领域广受欢迎,在数据分析、人工智能等领域也大放异彩。在药物研发中,...
数据库与生物信息学:基因数据挖掘与分析
生物信息学是一个跨学科的领域,融合了生物学、计算机科学和统计学的知识,旨在利用计算机和统计学方法来处理和分析生物学数据。随着高通量测序技术的快速发展,大量的基因数据不断产生,给研究人员带来了巨大的挑战...
Python在流行病学研究中的数据分析工具
这一章节旨在为读者提供Python数据分析的起点,涵盖其基本概念和工作流程,为后续深入讨论数据处理和应用分析奠定基础。 Python数据分析的旅程始于了解其在科学计算和数据处理中的角色。Python强大的生态系统,如...
CSDN会员
开通CSDN年卡参与万元壕礼抽奖
海量
VIP免费资源
千本
正版电子书
商城
会员专享价
千门
课程&专栏
全年可省5,000元
立即开通
全年可省5,000元
立即开通
大家在看
伺服环修正参数-Power PMAC
伺服环修正参数 Ix59: 用户自写伺服/换向算法 使能 =0: 使用标准PID算法, 标准换向算法 =1: 使用自写伺服算法, 标准换向算法 =2: 使用标准PID算法,自写换向算法 =3: 使用自写伺服算法,自写换向算法 Ix60: 伺服环周期扩展 每 (Ix60+1) 个伺服中断闭环一次 用于慢速,低分辨率的轴 用于处理控制 “轴” NEW IDEAS IN MOTION
微软--项目管理软件质量控制实践篇(一)(二)(三)
因为工作在微软的缘故,无论我在给国内企业做软件测试内训的时候,还是在质量技术大会上做演讲的时候,问的最多的一个问题就是:微软如何做测试的?前几天看见有人在新浪微博上讨论是否需要专职QA,再有我刚刚决定带领两个google在西雅图的测试工程师一起翻译google的新书《howgoogletestssoftware》。微软以前也有一本书《howwetestsoftwareatmicrosoft》。所以几件事情碰到一起,有感而发,决定写一个“xx公司如何测试的”系列文章。目的不是为了回答以上问题,旨在通过分析对比如Microsoft,Google,Amazon,Facebook等在保证产品质量的诸多
robotstudio sdk二次开发 自定义组件 Logger输出和加法器(C#代码和学习笔记)
图书robotstudio sdk二次开发中第4章 第4节 自定义组件 Logger输出和加法器,C#写的代码,和本人实现截图
chfenger-Waverider-master0_乘波体_
对乘波体进行建模,可以通过in文件输入马赫数、内锥角等参数,得到锥导乘波体的坐标点
宽带信号下阻抗失配引起的群时延变化的一种计算方法 (2015年)
在基于时延测量的高精度测量设备中,对群时延测量的精度要求非常苛刻。在电路实现的过程中,阻抗失配是一种必然存在的现象,这种现象会引起信号传输过程中群时延的变化。电路实现过程中影响阻抗的一个很重要的现象便是趋肤效应,因此在研究阻抗失配对群时延影响时必须要考虑趋肤效应对阻抗的影响。结合射频电路理论、传输线理路、趋肤效应理论,提出了一种宽带信号下阻抗失配引起的群时延变化的一种方法。并以同轴电缆为例进行建模,利用Matlab软件计算该方法的精度并与ADS2009软件的仿真结果进行比对。群时延精度在宽带信号下可达5‰
最新推荐
基于hadoop的百度云盘源代码(亲测可用完整项目代码)
基于hadoop的百度云盘源代码(亲测可用完整项目代码),个人经导师指导并认可通过的毕业设计项目,评审分98分,项目中的源码都是经过本地编译过可运行的,都经过严格调试,确保可以运行!主要针对计算机相关专业的正在做毕业设计的学生和需要项目实战练习的学习者,资源项目的难度比较适中,内容都是经过助教老师审定过的能够满足学习、使用需求,如果有需要的话可以放心下载使用。 基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的百度云盘源代码(亲测可用完整项目代码)基于hadoop的
HTML挑战:30天技术学习之旅
资源摘要信息: "desafio-30dias" 标题 "desafio-30dias" 暗示这可能是一个与挑战或训练相关的项目,这在编程和学习新技能的上下文中相当常见。标题中的数字“30”很可能表明这个挑战涉及为期30天的时间框架。此外,由于标题是西班牙语,我们可以推测这个项目可能起源于或至少是针对西班牙语使用者的社区。标题本身没有透露技术上的具体内容,但挑战通常涉及一系列任务,旨在提升个人的某项技能或知识水平。 描述 "desafio-30dias" 并没有提供进一步的信息,它重复了标题的内容。因此,我们不能从中获得关于项目具体细节的额外信息。描述通常用于详细说明项目的性质、目标和期望成果,但由于这里没有具体描述,我们只能依靠标题和相关标签进行推测。 标签 "HTML" 表明这个挑战很可能与HTML(超文本标记语言)有关。HTML是构成网页和网页应用基础的标记语言,用于创建和定义内容的结构、格式和语义。由于标签指定了HTML,我们可以合理假设这个30天挑战的目的是学习或提升HTML技能。它可能包含创建网页、实现网页设计、理解HTML5的新特性等方面的任务。 压缩包子文件的文件名称列表 "desafio-30dias-master" 指向了一个可能包含挑战相关材料的压缩文件。文件名中的“master”表明这可能是一个主文件或包含最终版本材料的文件夹。通常,在版本控制系统如Git中,“master”分支代表项目的主分支,用于存放项目的稳定版本。考虑到这个文件名称的格式,它可能是一个包含所有相关文件和资源的ZIP或RAR压缩文件。 结合这些信息,我们可以推测,这个30天挑战可能涉及了一系列的编程任务和练习,旨在通过实践项目来提高对HTML的理解和应用能力。这些任务可能包括设计和开发静态和动态网页,学习如何使用HTML5增强网页的功能和用户体验,以及如何将HTML与CSS(层叠样式表)和JavaScript等其他技术结合,制作出丰富的交互式网站。 综上所述,这个项目可能是一个为期30天的HTML学习计划,设计给希望提升前端开发能力的开发者,尤其是那些对HTML基础和最新标准感兴趣的人。挑战可能包含了理论学习和实践练习,鼓励参与者通过构建实际项目来学习和巩固知识点。通过这样的学习过程,参与者可以提高在现代网页开发环境中的竞争力,为创建更加复杂和引人入胜的网页打下坚实的基础。
【CodeBlocks精通指南】:一步到位安装wxWidgets库(新手必备)
 # 摘要 本文旨在为使用CodeBlocks和wxWidgets库的开发者提供详细的安装、配置、实践操作指南和性能优化建议。文章首先介绍了CodeBlocks和wxWidgets库的基本概念和安装流程,然后深入探讨了CodeBlocks的高级功能定制和wxWidgets的架构特性。随后,通过实践操作章节,指导读者如何创建和运行一个wxWidgets项目,包括界面设计、事件
andorid studio 配置ERROR: Cause: unable to find valid certification path to requested target
### 解决 Android Studio SSL 证书验证问题 当遇到 `unable to find valid certification path` 错误时,这通常意味着 Java 运行环境无法识别服务器提供的 SSL 证书。解决方案涉及更新本地的信任库或调整项目中的网络请求设置。 #### 方法一:安装自定义 CA 证书到 JDK 中 对于企业内部使用的私有 CA 颁发的证书,可以将其导入至 JRE 的信任库中: 1. 获取 `.crt` 或者 `.cer` 文件形式的企业根证书; 2. 使用命令行工具 keytool 将其加入 cacerts 文件内: ```
VC++实现文件顺序读写操作的技巧与实践
资源摘要信息:"vc++文件的顺序读写操作" 在计算机编程中,文件的顺序读写操作是最基础的操作之一,尤其在使用C++语言进行开发时,了解和掌握文件的顺序读写操作是十分重要的。在Microsoft的Visual C++(简称VC++)开发环境中,可以通过标准库中的文件操作函数来实现顺序读写功能。 ### 文件顺序读写基础 顺序读写指的是从文件的开始处逐个读取或写入数据,直到文件结束。这与随机读写不同,后者可以任意位置读取或写入数据。顺序读写操作通常用于处理日志文件、文本文件等不需要频繁随机访问的文件。 ### VC++中的文件流类 在VC++中,顺序读写操作主要使用的是C++标准库中的fstream类,包括ifstream(用于从文件中读取数据)和ofstream(用于向文件写入数据)两个类。这两个类都是从fstream类继承而来,提供了基本的文件操作功能。 ### 实现文件顺序读写操作的步骤 1. **包含必要的头文件**:要进行文件操作,首先需要包含fstream头文件。 ```cpp #include <fstream> ``` 2. **创建文件流对象**:创建ifstream或ofstream对象,用于打开文件。 ```cpp ifstream inFile("example.txt"); // 用于读操作 ofstream outFile("example.txt"); // 用于写操作 ``` 3. **打开文件**:使用文件流对象的成员函数open()来打开文件。如果不需要在创建对象时指定文件路径,也可以在对象创建后调用open()。 ```cpp inFile.open("example.txt", std::ios::in); // 以读模式打开 outFile.open("example.txt", std::ios::out); // 以写模式打开 ``` 4. **读写数据**:使用文件流对象的成员函数进行数据的读取或写入。对于读操作,可以使用 >> 运算符、get()、read()等方法;对于写操作,可以使用 << 运算符、write()等方法。 ```cpp // 读取操作示例 char c; while (inFile >> c) { // 处理读取的数据c } // 写入操作示例 const char *text = "Hello, World!"; outFile << text; ``` 5. **关闭文件**:操作完成后,应关闭文件,释放资源。 ```cpp inFile.close(); outFile.close(); ``` ### 文件顺序读写的注意事项 - 在进行文件读写之前,需要确保文件确实存在,且程序有足够的权限对文件进行读写操作。 - 使用文件流进行读写时,应注意文件流的错误状态。例如,在读取完文件后,应检查文件流是否到达文件末尾(failbit)。 - 在写入文件时,如果目标文件不存在,某些open()操作会自动创建文件。如果文件已存在,open()操作则会清空原文件内容,除非使用了追加模式(std::ios::app)。 - 对于大文件的读写,应考虑内存使用情况,避免一次性读取过多数据导致内存溢出。 - 在程序结束前,应该关闭所有打开的文件流。虽然文件流对象的析构函数会自动关闭文件,但显式调用close()是一个好习惯。 ### 常用的文件操作函数 - `open()`:打开文件。 - `close()`:关闭文件。 - `read()`:从文件读取数据到缓冲区。 - `write()`:向文件写入数据。 - `tellg()` 和 `tellp()`:分别返回当前读取位置和写入位置。 - `seekg()` 和 `seekp()`:设置文件流的位置。 ### 总结 在VC++中实现顺序读写操作,是进行文件处理和数据持久化的基础。通过使用C++的标准库中的fstream类,我们可以方便地进行文件读写操作。掌握文件顺序读写不仅可以帮助我们在实际开发中处理数据文件,还可以加深我们对C++语言和文件I/O操作的理解。需要注意的是,在进行文件操作时,合理管理和异常处理是非常重要的,这有助于确保程序的健壮性和数据的安全。
【大数据时代必备:Hadoop框架深度解析】:掌握核心组件,开启数据科学之旅
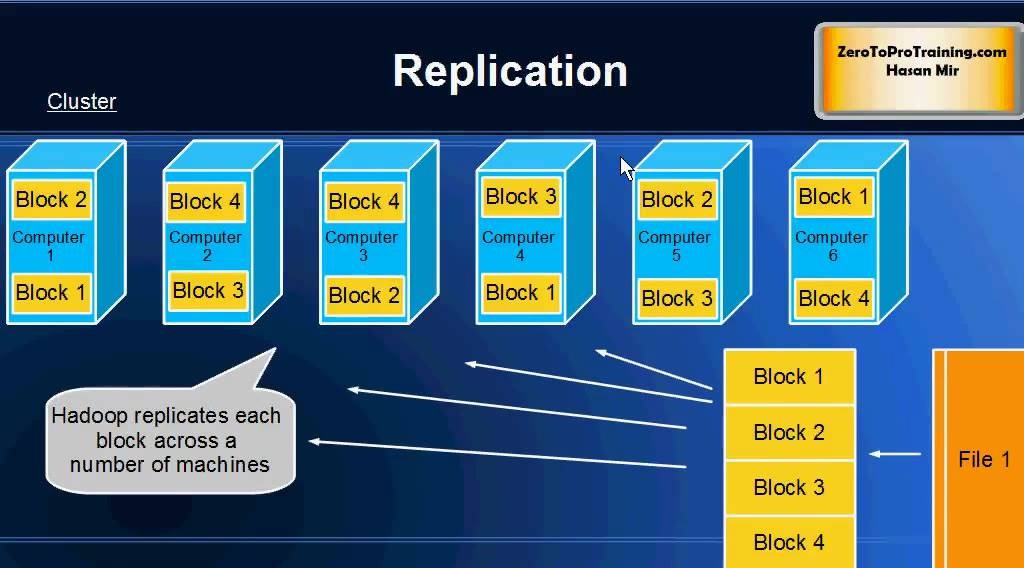 # 摘要 Hadoop作为一个开源的分布式存储和计算框架,在大数据处理领域发挥着举足轻重的作用。本文首先对Hadoop进行了概述,并介绍了其生态系统中的核心组件。深入分
opencv的demo程序
### OpenCV 示例程序 #### 图像读取与显示 下面展示如何使用 Python 接口来加载并显示一张图片: ```python import cv2 # 加载图像 img = cv2.imread('path_to_image.jpg') # 创建窗口用于显示图像 cv2.namedWindow('image', cv2.WINDOW_AUTOSIZE) # 显示图像 cv2.imshow('image', img) # 等待按键事件 cv2.waitKey(0) # 销毁所有创建的窗口 cv2.destroyAllWindows() ``` 这段代码展示了最基本的图
NeuronTransportIGA: 使用IGA进行神经元材料传输模拟
资源摘要信息:"matlab提取文件要素代码-NeuronTransportIGA:该软件包使用等几何分析(IGA)在神经元的复杂几何形状中执行材料传输模拟" 标题中提到的"NeuronTransportIGA"是一个使用等几何分析(Isogeometric Analysis, IGA)技术的软件包,该技术在处理神经元这样复杂的几何形状时进行材料传输模拟。等几何分析是一种新兴的数值分析方法,它利用与计算机辅助设计(CAD)相同的数学模型,从而提高了在仿真中处理复杂几何结构的精确性和效率。 描述中详细介绍了NeuronTransportIGA软件包的使用流程,其中包括网格生成、控制网格文件的创建和仿真工作的执行。具体步骤包括: 1. 网格生成(Matlab):首先,需要使用Matlab代码对神经元骨架进行平滑处理,并生成用于IGA仿真的六面体控制网格。这里所指的“神经元骨架信息”通常以.swc格式存储,它是一种描述神经元三维形态的文件格式。网格生成依赖于一系列参数,这些参数定义在mesh_parameter.txt文件中。 2. 控制网格文件的创建:根据用户设定的参数,生成的控制网格文件是.vtk格式的,通常用于可视化和分析。其中,controlmesh.vtk就是最终生成的六面体控制网格文件。 在使用过程中,用户需要下载相关代码文件,并放置在meshgeneration目录中。接着,使用TreeSmooth.m代码来平滑输入的神经元骨架信息,并生成一个-smooth.swc文件。TreeSmooth.m脚本允许用户在其中设置平滑参数,影响神经元骨架的平滑程度。 接着,使用Hexmesh_main.m代码来基于平滑后的神经元骨架生成六面体网格。Hexmesh_main.m脚本同样需要用户设置网格参数,以及输入/输出路径,以完成网格的生成和分叉精修。 此外,描述中也提到了需要注意的“笔记”,虽然具体笔记内容未给出,但通常这类笔记会涉及到软件包使用中可能遇到的常见问题、优化提示或特殊设置等。 从标签信息“系统开源”可以得知,NeuronTransportIGA是一个开源软件包。开源意味着用户可以自由使用、修改和分发该软件,这对于学术研究和科学计算是非常有益的,因为它促进了研究者之间的协作和知识共享。 最后,压缩包子文件的文件名称列表为"NeuronTransportIGA-master",这表明了这是一个版本控制的源代码包,可能使用了Git版本控制系统,其中"master"通常是指默认的、稳定的代码分支。 通过上述信息,我们可以了解到NeuronTransportIGA软件包不仅仅是一个工具,它还代表了一个研究领域——即使用数值分析方法对神经元中的物质传输进行模拟。该软件包的开发和维护为神经科学、生物物理学和数值工程等多个学科的研究人员提供了宝贵的资源和便利。
【Linux多系统管理大揭秘】:专家级技巧助你轻松驾驭
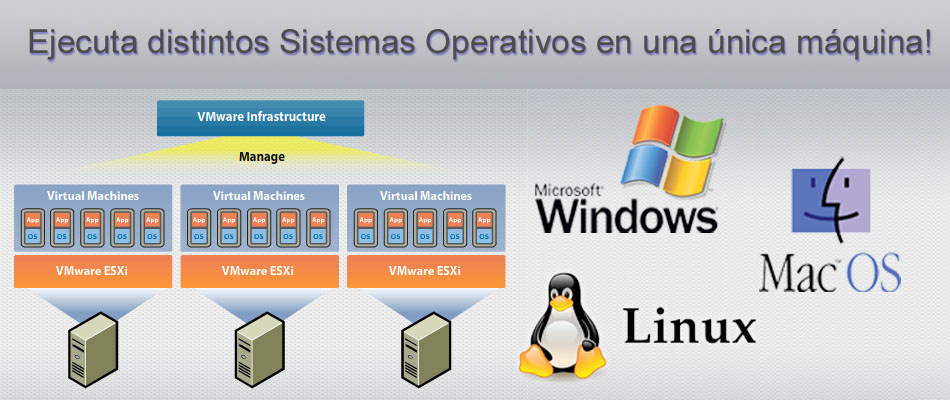 # 摘要 本文全面介绍了Linux多系统管理的关键技术和最佳实践。首先概述了多系统管理的基本概念,随后详细探讨了多系统的安装与启动流程,包括系统安装前的准备工作、各主流Linux发行版的安装方法以及启动管理器GRUB2的配置。接下来,文章深入分析了Linux多系统间文件共享与数据迁移的策略,特别是NTFS与Linux文件系统的互操作性和网络文件系统(NFS)的应用。此外,本
fofa和fofa viewer的区别
### Fofa与Fofa Viewer的区别 #### 功能特性对比 FoFA 是一个专注于安全研究的搜索引擎,能够帮助用户发现互联网上的各种资产信息。而 Fofa Viewer 则是一个基于 FoFA 的客户端应用,旨在简化 FoFA 的使用流程并提供更友好的用户体验[^1]。 - **搜索能力** - FoFA 提供了丰富的语法支持来精确查找特定条件下的网络资源。 - Fofa Viewer 将这些高级功能集成到了图形界面中,使得即使是初学者也能轻松执行复杂的查询操作[^2]。 - **易用性** - FoFA 主要面向有一定技术背景的安全研究人员和技术爱好者。 -