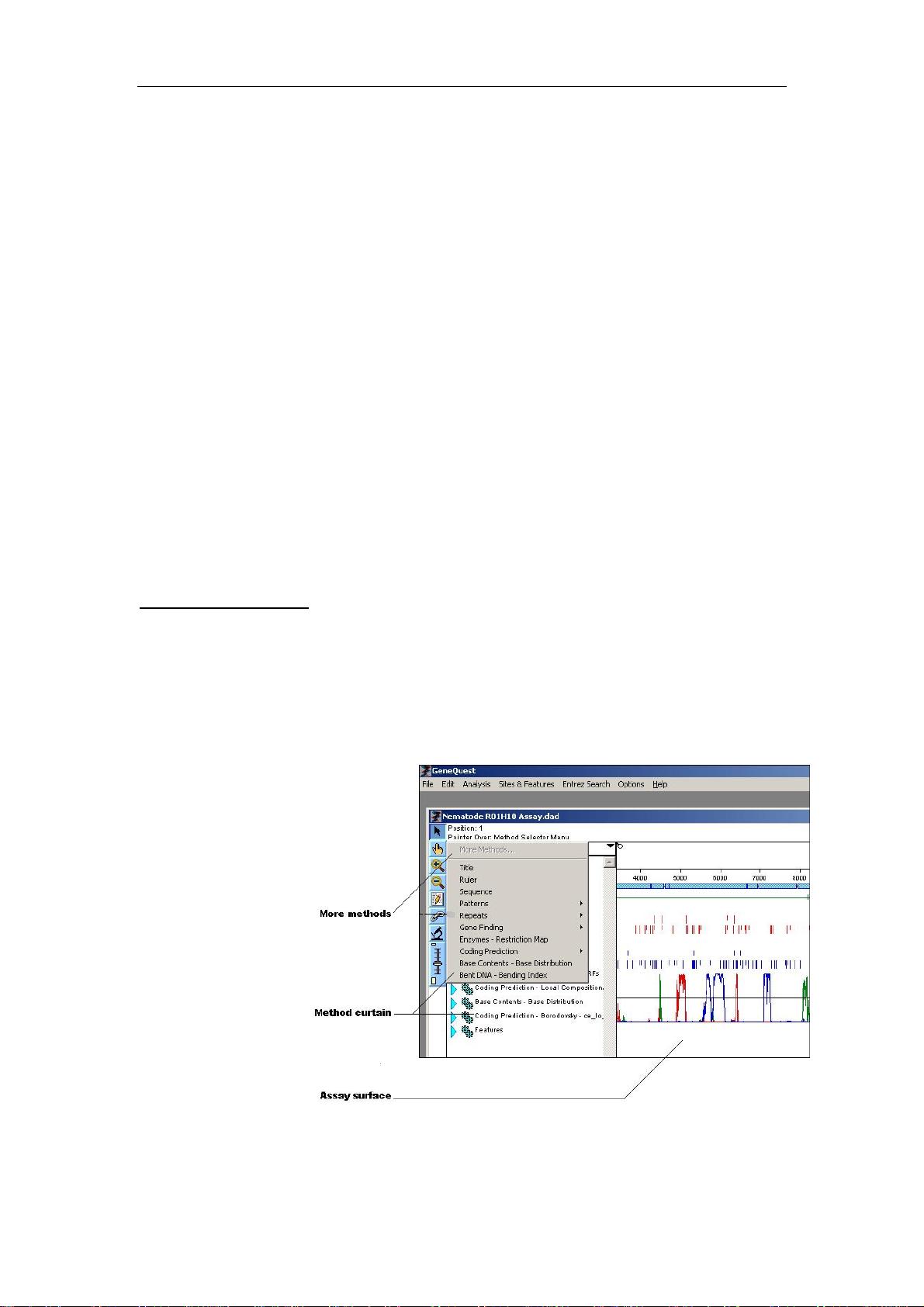
DNAStar软件中文使用指南:编辑、分析核酸序列
需积分: 39 119 浏览量
更新于2024-07-16
2
收藏 1.25MB PDF 举报
"DNAStar中文使用说明书,涵盖了EditSeq、MapDraw、MegAlign、PrimerSelect、Protean和SeqManII等模块的使用方法,包括打开和编辑序列、寻找开放读框、翻译DNA序列以及使用不同遗传密码等功能。"
DNAStar是一款专业用于生物核酸处理的软件,广泛应用于分子生物学领域。该软件提供了多个功能强大的模块,帮助科研人员进行序列分析和数据处理。以下是对这些模块的详细介绍:
1. **EditSeq**:这是DNAStar的基础序列编辑工具,用户可以打开并编辑DNA序列。例如,你可以通过`SetEnds`命令去除序列两端的污染序列。此外,EditSeq还支持查找开放读框(ORF)的功能,帮助确定可翻译的编码序列。
2. **MapDraw**:这个模块专注于序列映射和绘图,使得研究人员能够直观地展示和理解复杂序列结构,包括基因组组装和比较。
3. **MegAlign**:主要用于多序列比对,可以比较和分析多个序列的相似性和差异,对于研究基因进化和物种关系具有重要意义。
4. **PrimerSelect**:设计和评估PCR引物的工具,可以帮助研究人员选择合适的引物进行PCR反应,确保扩增出特定的目标序列。
5. **Protean**:专注于蛋白质结构和功能预测,包括二级结构分析、三级结构预测和蛋白质-蛋白质相互作用的模拟。
6. **SeqManII**:是一个全面的序列分析平台,提供从基本的序列质量检查到高级的序列拼接和分析。
在使用DNAStar时,用户可以根据需求选择相应的模块进行操作。例如,寻找开放读框是确定可能编码蛋白质的区域,这对于基因功能研究至关重要。而翻译DNA序列则涉及到将DNA序列转化为氨基酸序列,这有助于理解序列可能编码的蛋白质功能。此外,软件还允许用户选择不同的遗传密码,以适应不同生物体或实验条件下的翻译规则。
DNAStar提供了一整套的生物信息学工具,为分子生物学研究提供了强大且灵活的支持,无论是简单的序列编辑,还是复杂的序列分析任务,都能高效完成。
1946 浏览量
749 浏览量
178 浏览量
140 浏览量
335 浏览量
634 浏览量
1710 浏览量