微生物组分析入门:扩增子与宏基因组解析
需积分: 0 86 浏览量
更新于2024-08-05
收藏 1.05MB PDF 举报
"ProteinCell综述翻译稿1——微生物组学分析的实用指南"
本文主要探讨了微生物组研究中的两个关键分析领域:扩增子和宏基因组数据分析。随着高通量测序技术的迅速进步,微生物组学研究已经成为揭示生物多样性和生态系统功能的重要手段。然而,这一领域的复杂性和数据量的庞大对研究者提出了挑战。
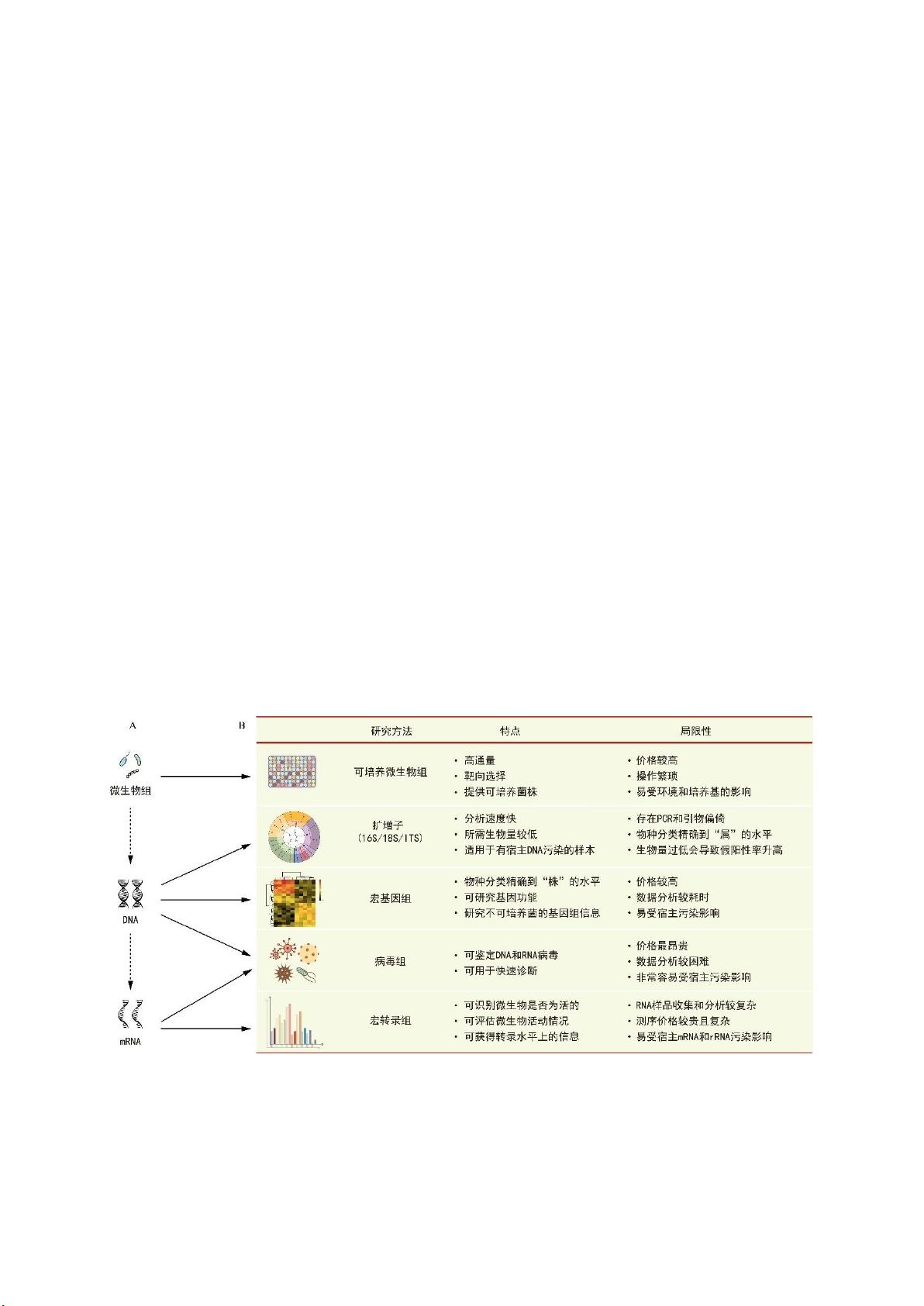
首先,文章介绍了微生物组常用测序技术,如扩增子测序和宏基因组测序。扩增子测序通常针对微生物的特定区域,如16S rRNA基因,用于鉴定和分类微生物种群。宏基因组测序则更全面,可以获取整个微生物群落的基因组信息,提供关于功能潜力的深入见解。每种技术都有其优势和局限性,选择哪种方法取决于研究目标和可用资源。
其次,文章推荐了一系列常用软件和分析流程,帮助研究者进行数据预处理、质量控制、比对、丰度计算、物种分类和功能注释。此外,还提到了重要的数据库,如 Silva 和 Greengenes 对于扩增子数据,以及 IMG/M 和 KEGG 对于宏基因组数据。
接着,文章详细阐述了微生物组分析的关键步骤。包括多样性分析,用于评估群落的丰富度和均匀度;物种组成分析,揭示不同样本间的微生物分布差异;差异分析,识别在不同条件或群体间显著变化的物种;相关分析,探究微生物群落成员之间的相互作用;网络分析,构建物种间的关联网络;机器学习方法,用于预测微生物群落结构与环境因素的关系;进化分析,研究微生物的系统发育关系;来源追溯,推断微生物的生态来源;以及各种可视化方法,如箱线图、热图和网络图,以直观展示分析结果。
为了保证研究的可重复性,文章还强调了实验设计、数据共享和分析流程记录的重要性。遵循良好的可重复性实践能够增强研究的可信度,促进科学界的共识和进步。
总结来说,这篇综述提供了微生物组学研究的实用指南,涵盖了从数据生成到解读的全过程。对于新进研究者而言,它是一份宝贵的资源,有助于他们理解并掌握微生物组数据分析的关键技术和策略,从而更好地挖掘数据背后的生物学意义。关键词涵盖了微生物组、宏基因组、标记基因测序、分析方法、流程、可重复性及可视化等方面,显示了该文的全面性和专业性。
2024-10-23 上传
2024-10-23 上传
2024-10-23 上传
2024-10-23 上传
丛乐
- 粉丝: 37
- 资源: 312
最新资源
- 单片机串口通信仿真与代码实现详解
- LVGL GUI-Guider工具:设计并仿真LVGL界面
- Unity3D魔幻风格游戏UI界面与按钮图标素材详解
- MFC VC++实现串口温度数据显示源代码分析
- JEE培训项目:jee-todolist深度解析
- 74LS138译码器在单片机应用中的实现方法
- Android平台的动物象棋游戏应用开发
- C++系统测试项目:毕业设计与课程实践指南
- WZYAVPlayer:一个适用于iOS的视频播放控件
- ASP实现校园学生信息在线管理系统设计与实践
- 使用node-webkit和AngularJS打造跨平台桌面应用
- C#实现递归绘制圆形的探索
- C++语言项目开发:烟花效果动画实现
- 高效子网掩码计算器:网络工具中的必备应用
- 用Django构建个人博客网站的学习之旅
- SpringBoot微服务搭建与Spring Cloud实践