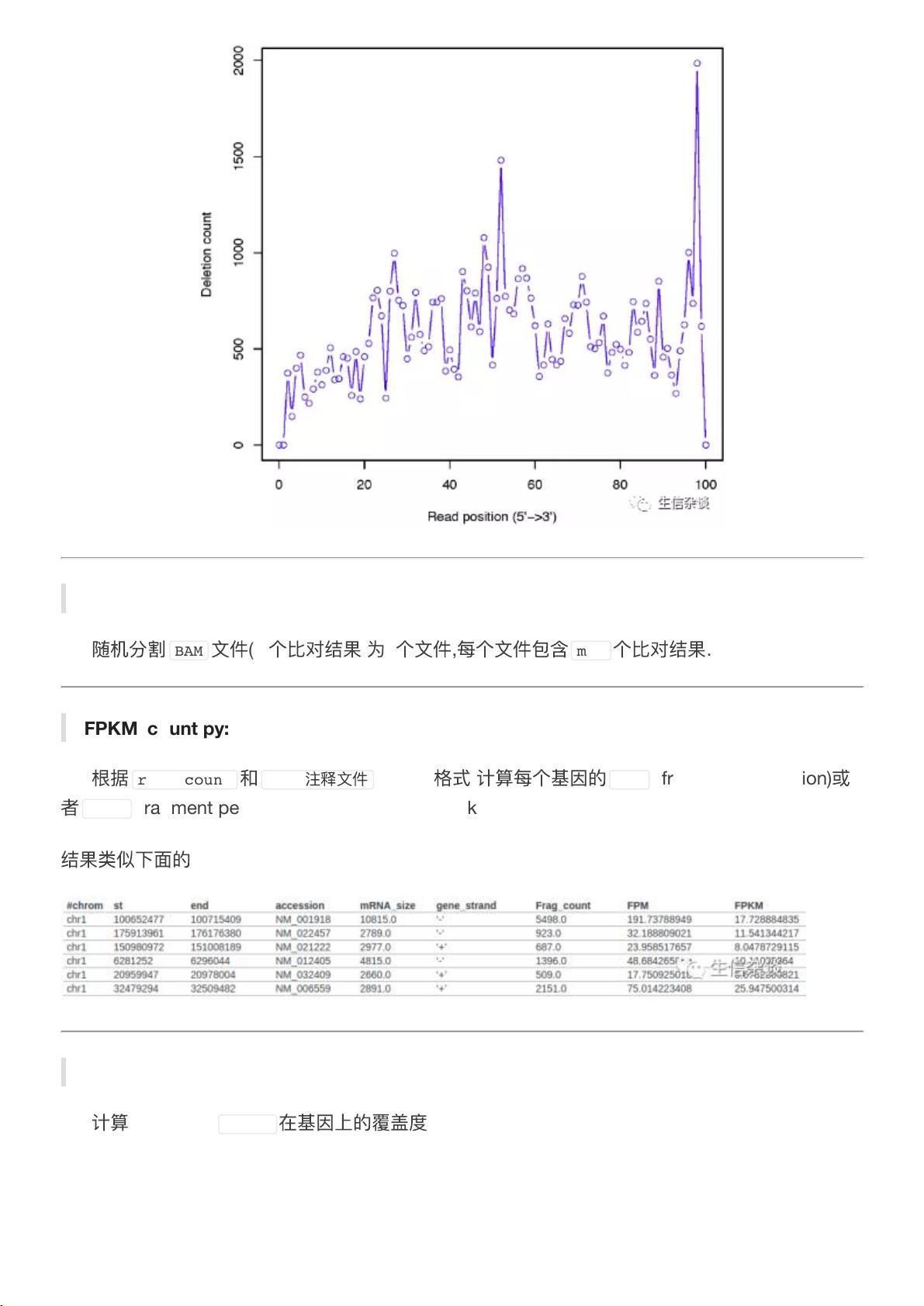
"高通量测序质控及可视化工具包RSeQC1"
高通量测序质控及可视化工具包RSeQC是一款专门用于评估高通量测序数据质量,特别是RNA-seq数据的工具集。该工具包提供了多种实用的小工具,用于分析序列质量、检测各种偏性(如核酸组分偏性、PCR偏性、GC含量偏性),并针对RNA-seq特性进行更深入的评估,如测序饱和度、映射读数分布、覆盖均匀性、链特异性以及转录水平的RNA完整性。
RSeQC依赖Python环境,用户可以通过Python的包管理器pip进行安装,命令为`pip install RSeQC`。该工具支持四种主要的输入文件格式:
1. BED格式:用于表示基因模型的12列纯文本文件。
2. SAM或BAM格式:SAM是可读的比对结果文本文件,而BAM是其压缩且可索引的版本,通常用于存储大量比对信息。
3. 染色体大小文件:包含两列的纯文本文件,用于指定参考基因组的各染色体长度。
4. Fasta文件:用于存储DNA序列的文件格式。
RSeQC的最新版本(2.6.4)包含了多个独立模块,可以单独调用执行不同的分析任务。例如,`bam2fq.py`模块可以从BAM文件中提取原始FASTQ序列数据。除此之外,其他模块可能包括:
- `quality_control`模块:用于评估序列质量,检查是否存在低质量碱基或短读长等问题。
- `junction_saturation`模块:评估RNA-seq数据的测序饱和度,判断是否达到足够的深度以捕捉所有剪接事件。
- `gene_coverage`模块:分析基因区域的覆盖度,确保测序数据在基因全长上的分布均匀。
- `strand_specificity`模块:检测链特异性,即确定读取是来自DNA分子的正链还是负链,这对于理解RNA表达和剪接至关重要。
- `splice_profile`模块:分析剪接位点的分布和使用情况。
- `duplication_rate`模块:计算重复读数的比例,帮助识别潜在的PCR偏好性。
这些模块的输出通常包括统计报告和可视化图表,有助于研究人员直观地了解数据质量和实验效果。通过RSeQC,用户能够全面地评估和优化他们的测序数据,从而提高后续分析的准确性和可靠性。在进行RNA-seq数据分析时,RSeQC是一个不可或缺的工具,能帮助确保数据质量,并为后续的转录组学研究提供坚实的基础。